这篇文章将为大家详细讲解有关R语言如何通过平行包实现多线程运行方式,小编觉得挺实用的,因此分享给大家做个参考,希望大家阅读完这篇文章后可以有所收获。
R语言是用于统计分析,绘图的语言和操作环境,属于GNU系统的一个自由,免费,源代码开放的软件,它是一个用于统计计算和统计制图的优秀工具。
总的来说,R的运算速度不算快,不过类似并行运算之类的改进可以提高运算的性能。下面非常简要地介绍如何利用R语言进行并行运算
detectCores()检查当前电脑可用核数。
makeCluster (cl.cores)使用刚才检测的核并行运算.R-Doc里这样描述makeCluster函数:创建一个组R并联运行的副本和通过套接字进行通信。即同时创建数个R进行并行运算。
在该函数执行后就已经开始并行运算了,电脑可能会变卡一点。尤其在执行par开头的函数时。
在并行运算环境下,常用的一些计算方法如下:
1。clusterEvalQ (cl, expr)函数利用创建的cl执行expr
这里利用刚才创建的cl核并行运算expr.expr是执行命令的语句,不过如果命令太长的话,一般写到文件里比较好。比如把想执行的命令放在Rcode。r里:
2。par开头的apply函数族
这族函数和apply的用法基本一样,不过要多加一个参数cl。一般如果cl创建如上面cl <- makeCluster(cl.cores)的话,这个参数可以直接用作parApply(cl=cl,…)。
当然Apply也可以是Sapply,Lapply等等。注意par后面的第一个字母是要大写的,而一般的apply函数族第一个字母不大写。另外要注意,即使构建了并行运算的核,不使用parApply()函数,而使用apply()函数的话,则仍然没有实现并行运算。
换句话说,makeCluster只是创建了待用的核,而不是并行运算的环境。
最后,终止并行运算只需要一行命令
stopCluster(cl)
案例1
不使用并行计算,直接使用lapply(隐式循环函数,它实际就是对不同的数据应用了相同的函数):
fun <- function(x){return (x+1);}system.time({res <- lapply(1:5000000, fun);});user system elapsed21.42 1.74 25.70案例2
使用parallel包来加速
library(parallel)#打开四核,具体核数根据机器的核数决定cl <- makeCluster(getOption("cl.cores", 4));system.time({res <- parLapply(cl, 1:5000000, fun)});user system elapsed6.54 0.34 19.95#关闭并行计算stopCluster(cl);看看单核机器跑出来的结果:
user system elapsed29.30 9.23 97.22
所以,并非核数越多越好,看机器配置。
这个函数有两点要注意:
首先要先用detectCores函数确定系统核心数目,对于Window系统下的Intel I5或I7 处理器,一般使用detectCores(logical=F)来获得实际的物理核心数量。
由于这个函数使用的是调用Rscript的方式,这个例子里,对象被复制了三份,因此内存会吃的很厉害,在大数据条件就要小心使用。
案例3
在Linux下使用mclapply函数的效果如下:
mc <- getOption("mc.cores", 3)system.time({res <- mclapply(1:5000000, fun, mc.cores = mc);});user system elapsed6.657 0.500 7.181 stopCluster(cl);补充:R语言如何并行处理[parallel package][向量化操作并行优化]
使用数据,长下面这样:

方法:
使用parallel包,并行向量化处理,进一步提升原先向量化处理速度。
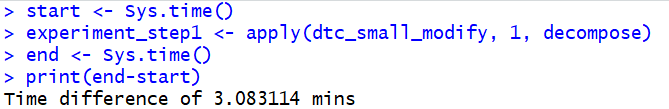
原始代码:
start <- Sys.time()experiment_step1 <- apply(dtc_small_modify, 1, decompose)end <- Sys.time()print(end-start)
原始运行时间:3.083114 分
使用parallel包后
library(parallel) #并行处理包cl.coresR语言如何通过平行包实现多线程运行方式