介绍
怎么使用肌肉进行多序列比,对针对这个问题,这篇文章详细介绍了相对应的分析和解答,希望可以帮助更多想解决这个问题的小伙伴找到更简单易行的方法。
肌肉是最为广泛使用的多序列比对工具之一,其速度和准确度比clustal都要更加优秀,在几秒钟的时间就可以完成上百条序列的比对,而且用法简单。
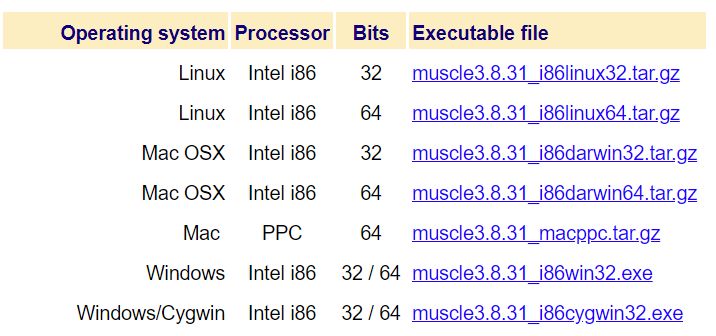
在下载页面,提供了多个操作系统的可执行文件。
 <李>
<李>
NJ
<李>UPGMA
NJ法构建的进化树可信度更高,而UPGMA建树的速度更快。基本用法如下
muscle -maketree 拷贝;seqs.afa -out seqs.phy -cluster neighborjoining
<代码>集群>
肌肉的默认参数设置最大化的保证了比对的准确度,对于大的序列,如果比对速度不是很理想时,可以适当的调整参数。
对于核酸和氨基酸序列,官方分别推荐了速度最快的参数设置。
核酸
muscle 拷贝;seqs.fa -out seqs.afa -maxiters 1, -diags
氨基酸
muscle 拷贝;seqs.fa -out seqs.afa -maxiters 1, -diags -sv -distance1 kbit20_3
使用肌肉时,其默认参数设置就能够满足绝大部分的使用场景,只有对于较大的输入序列时,才需要调整参数。
EBI提供了肌肉的在线服务,网址如下
https://www.ebi.ac.uk/Tools/msa/muscle/
用法和clustal的用法是类似的,这里就不赘述了。对于500条以下而且数据量小于1 mb的序列,可以直接使用该在线服务。
关于怎么使用肌肉进行多序列比对问题的解答就分享到这里了,希望以上内容可以对大家有一定的帮助,如果你还有很多疑惑没有解开,可以关注行业资讯频道了解更多相关知识。
怎么使用肌肉进行多序列比对





